Segmentation des tumeurs cérébrales en IRM par U-Net 3D (BraTS2020)
Ce projet porte sur la segmentation automatique des tumeurs cérébrales à partir d’images d’IRM multimodales, en s’appuyant sur les données du challenge BraTS2020. La segmentation précise des tumeurs est essentielle pour le diagnostic et le suivi des patients, mais reste une tâche complexe en raison de la variabilité des structures tumorales et des caractéristiques des images médicales.
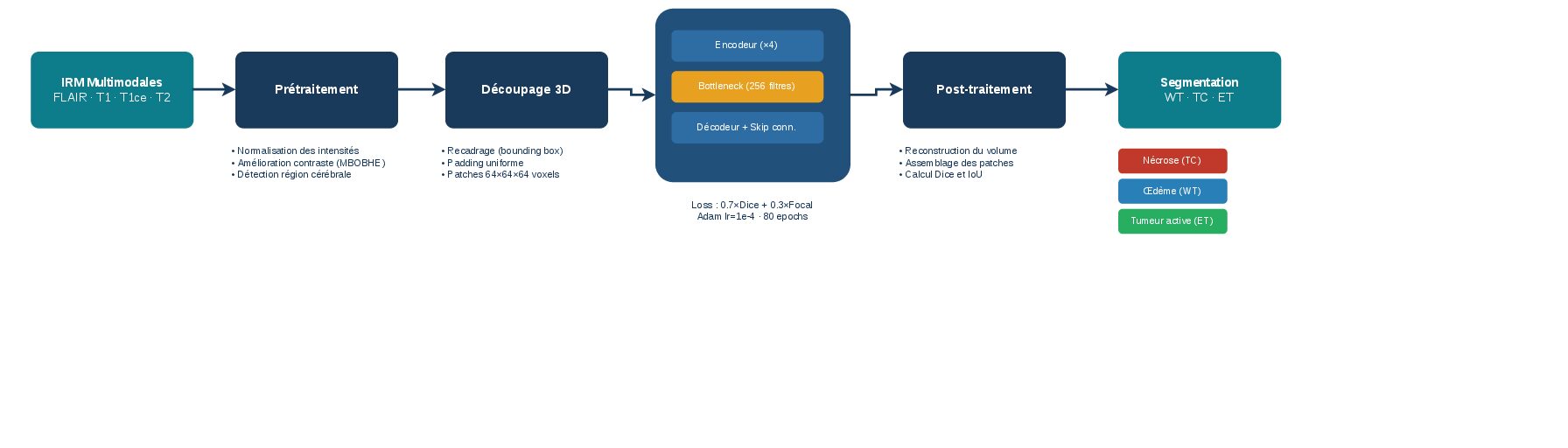
L’objectif de ce travail est de développer un modèle de deep learning capable de segmenter les différentes régions tumorales (nécrose, œdème et tumeur active) de manière automatique et fiable. Pour cela, un pipeline complet a été mis en place, incluant le prétraitement des images (normalisation, amélioration du contraste, recadrage) ainsi que le découpage en volumes 3D de taille 64×64×64.
Le modèle utilisé repose sur une architecture U-Net 3D, adaptée à la segmentation volumique. L’entraînement est optimisé à l’aide d’un générateur de données, d’une pondération des classes et d’une fonction de perte combinée afin de gérer le déséquilibre des données.
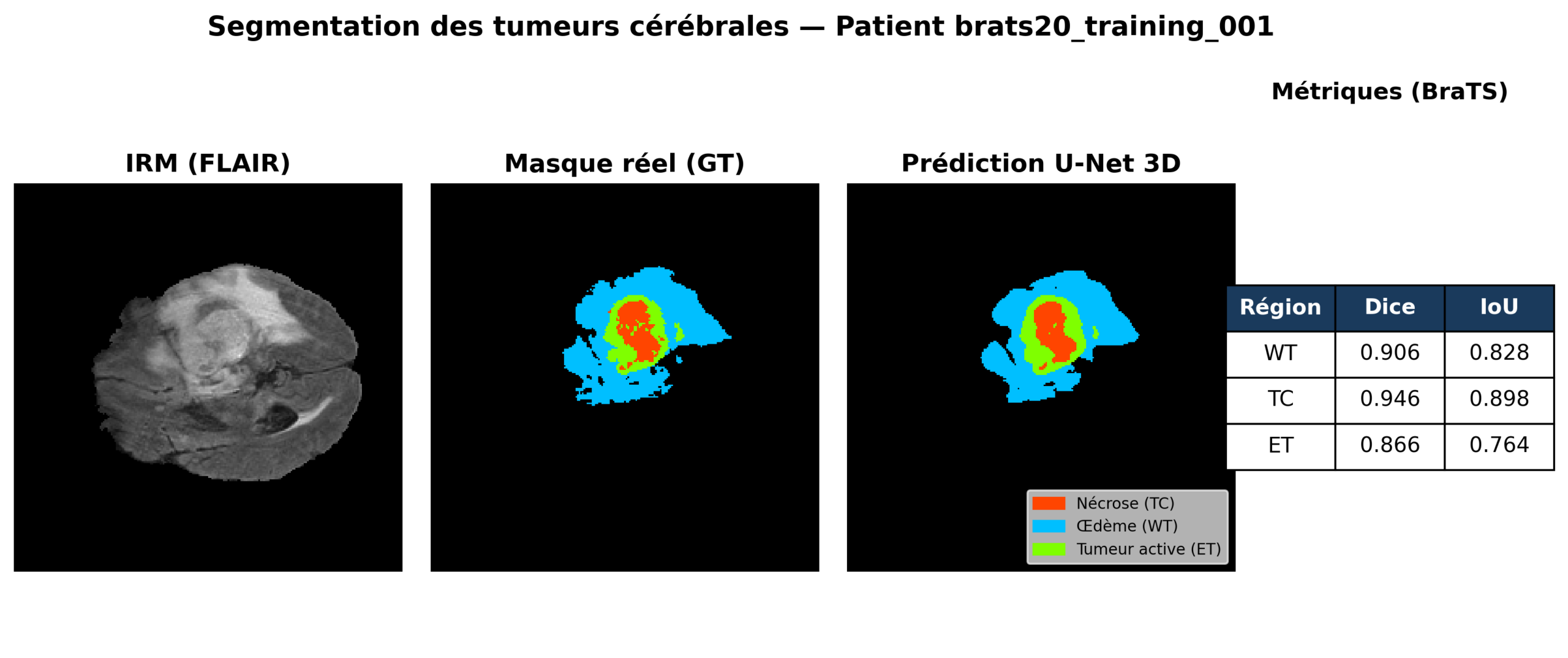
Les performances sont évaluées à l’aide des métriques officielles du challenge BraTS (Dice coefficient), avec des résultats de 0.83 pour la tumeur complète (WT), 0.72 pour le cœur tumoral (TC) et 0.73 pour la tumeur active (ET), indiquant des performances globalement satisfaisantes.
Ce travail démontre la pertinence des approches basées sur le deep learning pour la segmentation des tumeurs cérébrales et ouvre des perspectives d’amélioration, notamment par l’optimisation du modèle et l’intégration de techniques avancées.
Présenté par
Nazif Iyatan Hervé AGBEDOH